Strutture non canoniche del genoma (G-loop e R-loop a valle della RNA polimerasi II) si ritrovano nel genoma di cellule umane inducendo instabilità del genoma e attivazione di geni dell’immunità innata.
Temi di ricerca
La regolazione delle funzioni genomiche è un processo complesso che coinvolge diversi fattori proteici e acidi nucleici. Grazie soprattutto allo sviluppo di tecnologie di sequenziamento (note come Next Generation Sequencing, NGS), è diventato possibile studiare come particolari strutture secondarie degli acidi nucleici possano influenzare funzioni genomiche fondamentali come l'espressione genica, la replicazione del DNA, la ricombinazione e la stabilità del genoma. In questo contesto, la nostra ricerca si concentra su come da un lato le strutture del DNA non-B influenzino l'organizzazione della cromatina e la stabilità del genoma, e dall’altro come queste strutture siano regolate dalle DNA Topoisomerasi.
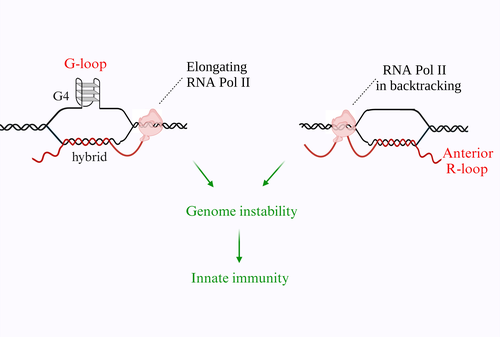
Siamo particolarmente interessati agli R-loop e ai G-quadruplex (G4). Gli R-loop si formano durante la trascrizione quando l'RNA nascente si riappaia al filamento di DNA stampo, formando un ibrido RNA:DNA e costringendo il filamento non-templato a restare a singolo filamento. I G4 sono invece generati da sequenze di DNA ricche di guanina a singolo filamento che si ripiegano in strutture stabili con quartetti planari impilati. Gli R-loop e i G4 sono strutture particolarmente sensibili ai superavvolgimenti di DNA. I superavvolgimenti negativi del DNA generati dietro una RNA polimerasi in fase di allungamento facilitano la formazione di R-loop. È interessante notare che i promotori attivi sono privi di nucleosomi, hanno più superavvolgimenti negativi rispetto ad altri siti genomici e sono regioni in cui gli R-loop e i G4 possono formarsi più facilmente. La DNA topoisomerasi I (Top1) è il principale fattore cellulare che controlla l'omeostasi topologica del genoma. Abbiamo quindi studiato il ruolo della TopI nella formazione degli R-loop in cellule umane mediante il silenziamento del gene o l'uso di inibitori specifici dell'attività di religazione dell’enzima. I risultati sono stati in qualche modo sorprendenti, in quanto dimostrano che la Top1 può effettivamente favorire o sfavorire la formazione degli R-loop a seconda del contesto cromatinico.
Recentemente abbiamo studiato il ruolo dei poison della Top1 nella generazione di micronuclei, con conseguente attivazione della via cGAS-STING e dell'espressione di geni immunitari nelle cellule tumorali. Inoltre, abbiamo dimostrato che questi composti possono attivare sia i geni IRF3- che quelli NF-kB-dipendenti, ma non possono farlo nelle cellule tumorali SCLC, poiché la via cGAS-STING è marcatamente compromessa, probabilmente a causa di diversi meccanismi, tra cui una drastica riduzione dell'espressione di STING e/o cGAS.
Ci siamo anche concentrati nel definire se la stabilizzazione chimica di G4 possa innescare la formazione di R-loop in cellule viventi. Abbiamo quindi eseguito diversi esperimenti per studiare gli effetti dei ligandi di G4 sulla formazione di R-loop e sull'integrità del genoma in cellule tumorali umane, utilizzando un metodo di immunoprecipitazione di R-loop (chiamato DRIP) e la tecnologia NGS. Abbiamo stabilito che i ligandi G4 inducono un aumento immediato degli R-loop nucleari, in quanto i G4 e gli R-loop possono cooperare e stabilizzarsi a vicenda durante la trascrizione, formando un G-loop. Inoltre, i dati dimostrano che i danni al DNA indotti dai ligandi G4 sono mediati dagli R-loop.
In sintesi, il nostro obiettivo di ricerca è stabilire meccanismi molecolari ed epigenetici dipendenti da strutture di DNA non-B di regolazione della trascrizione e instabilità del genoma.
